中國科學院南海海洋研究所熱帶海洋生物資源與生態實驗室(LMB)喻子牛研究員團隊在牡蠣高密度遺傳連鎖圖譜構建和殼生長QTL定位、功能基因驗證方面取得重要進展,相關研究成果High-resolution genetic maps and QTL mapping applications reveal Polycystin gene involvement in oyster shell formation正式發表于國際綜合期刊《iScience》。南海海洋研究所助理研究員馬海濤、副研究員秦艷平等為論文共同第一作者,研究員喻子牛和研究員張躍環為論文通訊作者。
香港牡蠣和熊本牡蠣是華南沿海重要的經濟優勢牡蠣種,團隊成功進行了兩種牡蠣間的人工遠緣雜交。本研究以兩種牡蠣正反交家系為材料,構建了它們的高密度遺傳連鎖圖譜。正交家系中母本(香港牡蠣)獲得了10個連鎖群,與其染色體數一致,標記間的平均間隔為1.5cM,圖譜總長度為899.37cM,圖譜的覆蓋率為97.30%;父本(熊本牡蠣)也獲得了10個連鎖群,與其染色體數一致,標記間的平均間隔、圖譜總長度、圖譜覆蓋率分別為1.22cM、836.94cM、97.40%。反交家系中母本(熊本牡蠣)獲得了10個連鎖群,與其染色體數一致,標記間的平均間隔為0.94cM,圖譜總長度為1096.09cM,圖譜的覆蓋率為98.63%;父本(香港牡蠣)獲得了10個連鎖群,與其染色體數一致,標記間的平均間隔、圖譜總長度、圖譜覆蓋率分別為1.23cM、653.36cM、97.04%。另外熊本牡蠣整合遺傳圖譜標記間的平均間隔達到0.75cM。
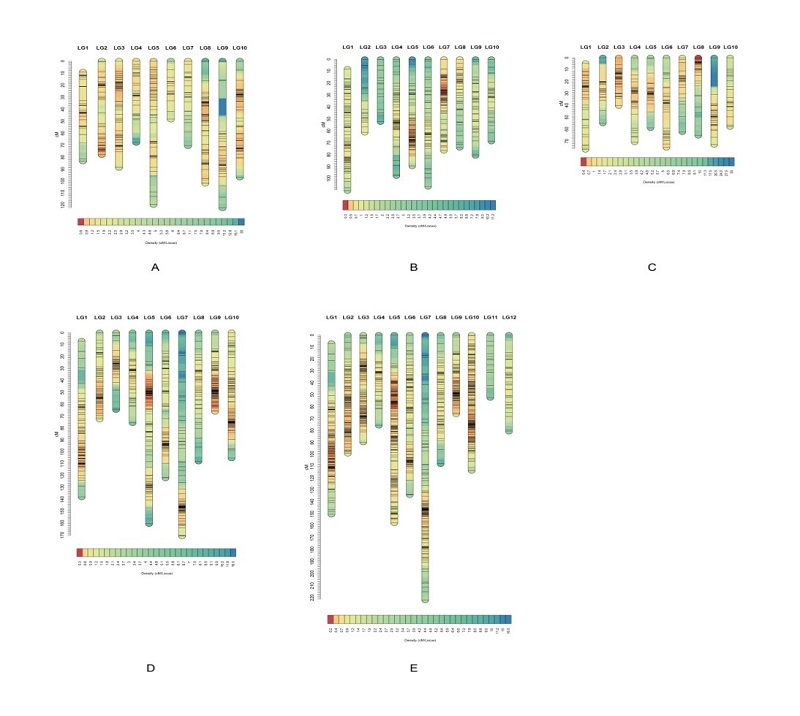
圖1 高密度遺傳連鎖圖譜
根據兩個作圖家系的表型數據和遺傳連鎖圖譜,共定位了35個與殼生長相關QTL位點,可解釋的表型遺傳變異為6.1-26.4%(殼高)、4.9-20.0%(殼長)。通過基因組基因比對,在QTL上共鑒定出22個候選基因,其中Polycystin基因具有最大LOD值和最高可解釋的表型變異(26.4%-殼高/20.0%-殼長)。
該成果在兩種牡蠣中首先克隆了Polycystin基因的全序列;q-PCR發現在牡蠣外套膜中表達水平最高,破殼試驗中其表達水平隨著貝殼形成過程發生變化,原位雜交也發現該基因表達于外套膜外褶和中褶邊緣區域;不同發育階段的定量表達分析,發現在兩種牡蠣中從受精卵開始表達量逐漸升高并在囊胚期達到最高峰,該基因可能參與了牡蠣殼早期發育的鈣離子儲存,為擔輪幼蟲及后期牡蠣殼發育提供基礎;RNAi技術成功抑制該基因表達后,通過掃描電鏡發現新生貝殼出現礦物層沉積不規則的現象。綜上所述,Polycystin基因很可能通過介導鈣離子運輸的方式參與了牡蠣殼形成。

圖2 功能驗證Polycystin基因參與了牡蠣殼形成
本研究首次構建了香港牡蠣和熊本牡蠣的高密度遺傳連鎖圖譜并定位了殼生長相關QTL位點,并證明Polycystin基因參與了牡蠣殼形成,研究結果將為兩種牡蠣的分子育種提供理論基礎和技術支撐。
該成果得到了廣東省自然科學基金、國家自然科學基金、國家貝類產業技術體系、科技部重點研發計劃、廣東省重點研發計劃、海南省重點研發計劃和廣州市重點研發計劃等項目的聯合資助。
相關論文信息:High-resolution genetic maps and QTL mapping applications reveal Polycystin gene involvement in oyster shell formation. iScience,2025,28: 113986.?
原文鏈接:https://doi.org/10.1016/j.isci.2025.113986
附件下載:


