




廣州健康院開發的scDIOR軟件打通單細胞組學R/Python平臺壁壘
1月6日,中國科學院廣州生物醫藥與健康研究院陳捷凱課題組開發的單細胞數據IO軟件“scDIOR”于BMC Bioinformatics雜志在線發表。該軟件統一了多種單細胞分析工具的數據結構,使單細胞數據能夠在不同平臺間快速轉換,減少存儲和內存消耗,將顯著提升單細胞研究的效率。
單細胞測序應用極廣,其數據具有樣本量大、信息量大、統計和挖掘極為復雜等特點,科學家往往需要不斷切換不同軟件,不同平臺來滿足分析需求。然而,單細胞數據在不同平臺之間的傳輸存在技術障礙,導致科學家將大量的時間花費在數據轉換上,嚴重影響研究效率。
為了解決上述問題,陳捷凱課題組開發了軟件scDIOR,統一了R和python平臺的三種主流的數據結構,即Seurat,SingleCellExperiment和Scanpy。通過scDIOR,單細胞數據以統一的H5格式保存,無論從哪個平臺開始,只需兩行代碼就可實現單細胞數據在不同工具包之間的快速轉換,支持轉錄組和空間組等多種數據類型(可繼續迭代增加),最大程度地保留了原始信息。因此,scDIOR可以快速比較一項分析任務在不同工具包的差異;依托H5文件格式的“組”,提供部分數據讀取功能,大幅度減少內存消耗和時間消耗;設計了命令行指令,可實現批量數據轉化。綜上所述,scDIOR可以應用建立一個標準的單細胞數據結構,將不同工具的優勢連接起來,幫助科學家更高效地完成單細胞的研究工作。
本研究在陳捷凱研究員和林立惠博士指導下,由生物島實驗室實習研究員馮輝堅完成。軟件已經過大量用戶使用優化,可在GitHub下載(鏈接 https://github.com/JiekaiLab/scDIOR),也歡迎提出寶貴意見(可發至feng_huijian@grmh-gdl.cn)。
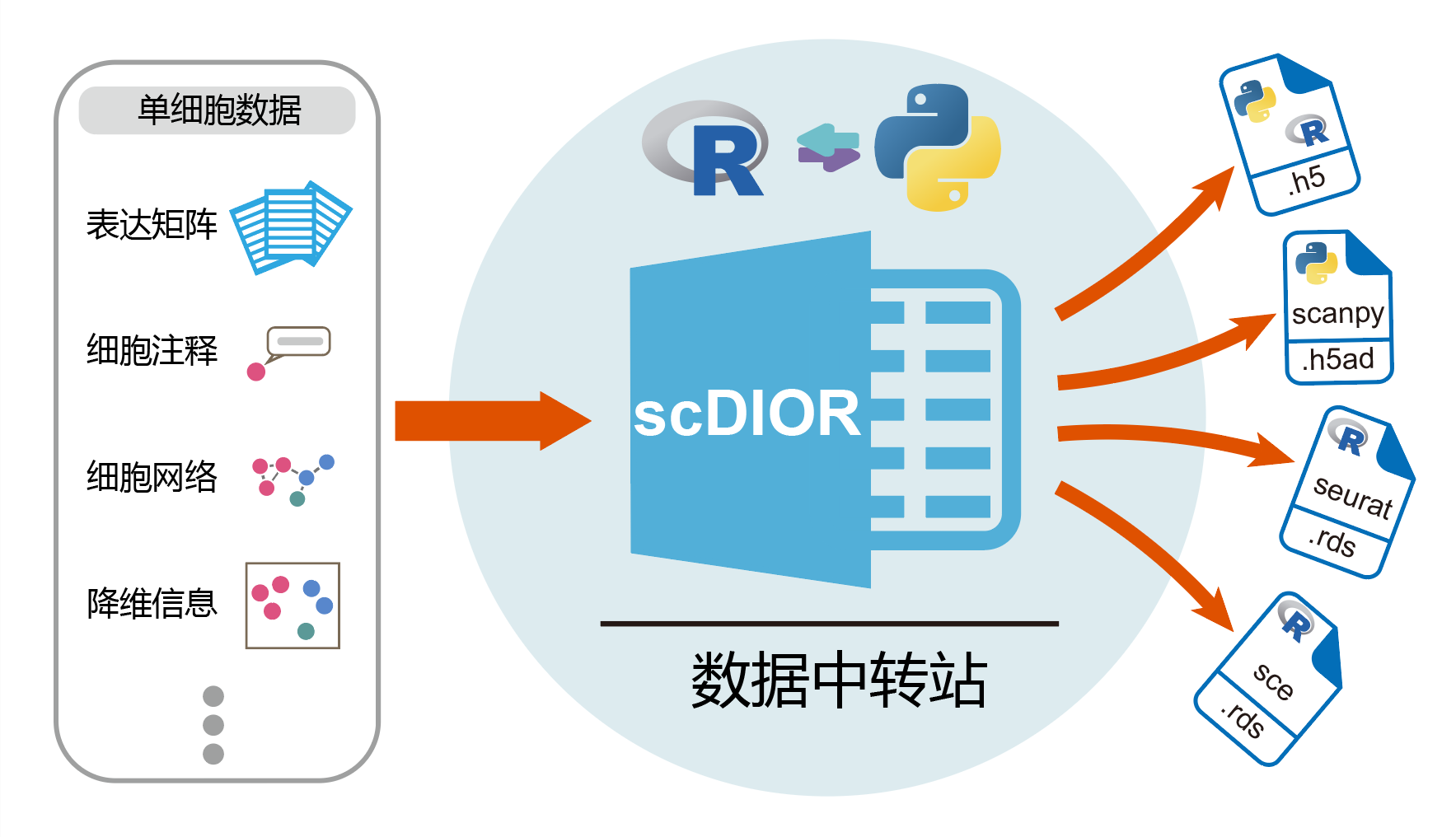
單細胞數據IO軟件scDIOR
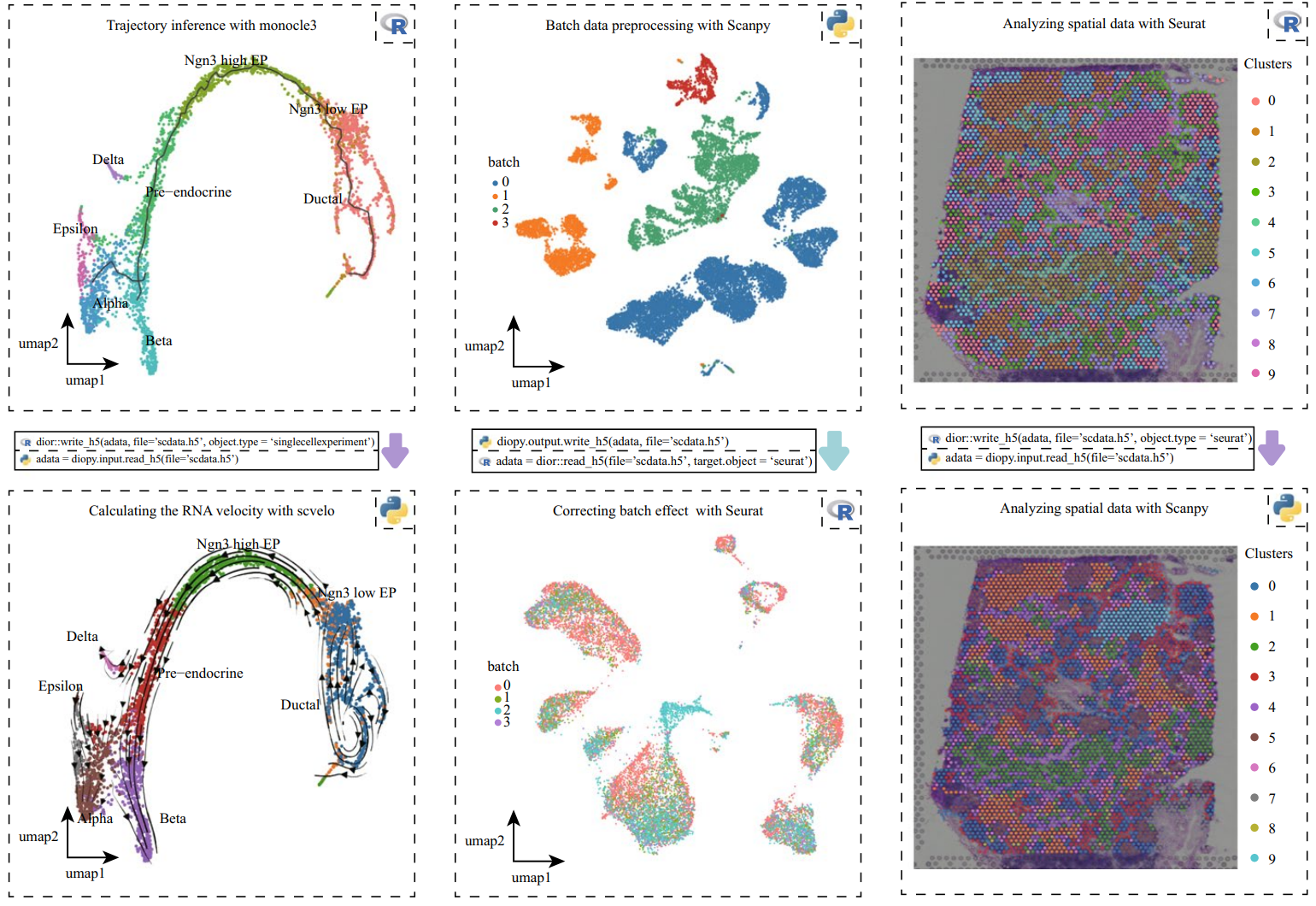
scDIOR很方便地實現數據在平臺間的轉換,將不同工具的優勢連接起來